给一个女孩取名叫做男孩她就可以去男厕所了吗
最近一个小伙伴反馈说他跟着官网的转录组测序数据表达量矩阵差异分析代码处理他自己的数据,报错了,但是我看了看他的提问,就非常诡异:
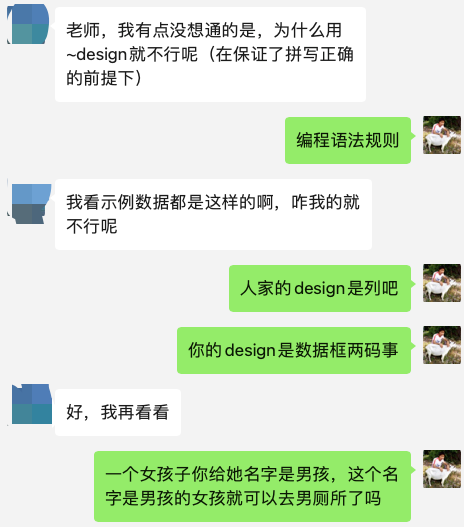
非常诡异的提问
首先是因为他仅仅是复制粘贴官方代码,而不考虑实际情况,官方代码里面确实是 design = ~ group,但是人家的 colData = metadata,,也就是说代码里面的group其实是 metadata这个数据框里面的一个列而已:

复制粘贴官方代码
而他自己构建的数据里面的metadata变量被改名为了 group,但是group里面的就两个列,之前的group其实是 metadata这个数据框里面的一个列,完全不一定性质。。。。
其实很容易查询到使用DESeq2包进行转录组表达量矩阵的差异分析的示例代码,超级简单的3个步骤而已。首先,你需要安装并加载DESeq2包:
if (!requireNamespace("BiocManager", quietly = TRUE))
install.packages("BiocManager")
BiocManager::install("DESeq2")
library(DESeq2)
dds <- DESeqDataSetFromMatrix(countData = countdata,
colData = coldata,
design = ~ condition)
dds <- DESeq(dds)
res <- results(dds)
然后,你需要创建一个DESeqDataSet对象。这通常需要两个输入:一个包含计数数据的矩阵和一个包含样本信息的data.frame。假设你的计数数据矩阵是countdata,样本信息是coldata,在这里,design参数定义了你的实验设计,~ condition表示你想要比较的条件。然后,你可以运行DESeq函数来进行差异表达分析:最后,你可以使用results函数来获取差异表达结果:
这将返回一个包含每个基因的log2 fold change(对数2倍变化),p值和调整后的p值的表。
所以小伙伴们给他的建议很简单,就是根据实际情况去修改 design = ~ group,它里面的group是数据框了,并不是之前的metadata这个数据框里面的一个列 :
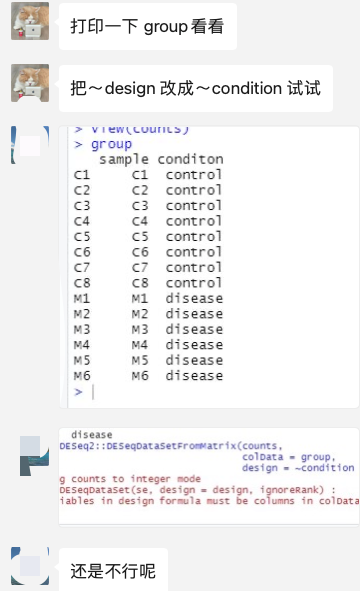
拼写问题
但是这个时候这个求助者又有一个错误,就是拼写问题,明明应该是condition这样的英文单词。
该如何避免编程时候的拼写问题呢?
避免编程时的拼写错误可以通过以下几种方式:
- 使用代码编辑器或集成开发环境(IDE):许多现代的代码编辑器和IDE,如Visual Studio Code,PyCharm,RStudio等,都有内置的拼写检查功能。这些工具可以在你输入代码时实时检查拼写错误,并提供修正建议。
- 使用代码规范和命名规则:一致的命名规则可以帮助你避免拼写错误。例如,你可以决定所有的变量名都使用小写字母和下划线,所有的函数名都使用驼峰命名法等。这样,当你看到一个不符合规则的名字时,你就知道可能有拼写错误。
- 使用自动补全功能:许多代码编辑器和IDE都有自动补全功能。当你开始输入一个变量或函数名时,编辑器会显示一个下拉列表,列出所有匹配的已知名字。这可以帮助你避免拼写错误。
- 代码审查:如果你在一个团队中工作,你可以让你的同事审查你的代码。他们可能会发现你没有注意到的拼写错误。
- 使用版本控制系统:使用如Git这样的版本控制系统可以帮助你追踪代码的变化。如果你发现了一个拼写错误,你可以很容易地回到之前的版本,找出错误是在哪里引入的。
- 经常测试和运行你的代码:这可以帮助你发现运行时错误,包括由拼写错误引起的问题。当你写完一个新的函数或模块后,应该立即测试它,确保它的行为符合你的预期。
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2023-06-22,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读
目录

