RNAseq | ComplexHeatmap绘制临床数据热图(所见即所得)
RNAseq | ComplexHeatmap绘制临床数据热图(所见即所得)

生信补给站
发布于 2024-04-24 15:52:01
发布于 2024-04-24 15:52:01
当使用各种机器学习方法(CoxBoost,Lasso,SuperPC,randomForestSRC,Elastic Net等)完成预后模型后,除了在组学层面( IPS评分,药物反应预测,WGCNA等)进行一系列的分析外,还可以将定义的风险得分和临床指标进行比较。如Expression of hub genes of endothelial cells in glioblastoma-A prognostic model for GBM patients integrating single-cell RNA sequencing and bulk RNA sequencing中下图所示
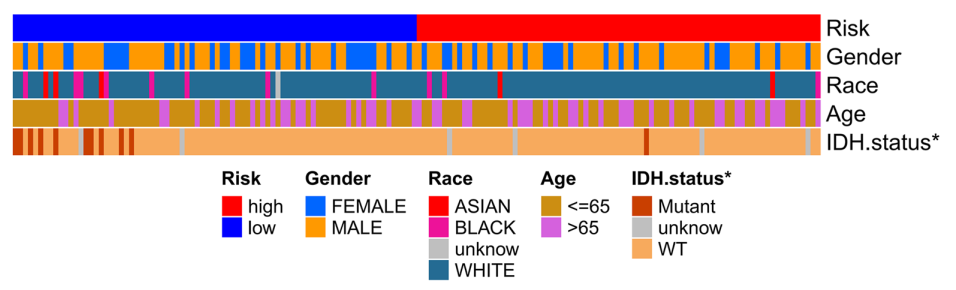
最初我完成该图的方法是用含有基因表达的热图,然后截图或者PS成只有临床指标。这里介绍使用ComplexHeatmap直接完成该图。
一 载入R包,数据
使用前面系列推文的TCGA-SKCM的临床数据和随访数据,以及经过lasso模型计算的风险评分结果 。
后台回复“临床”既可获取Expr_phe_cli_riskscore.RData的示例数据。
library(tidyverse)
library(ComplexHeatmap)
library(ggsci) #颜色
library(circlize) #连续颜色
#载入数据
load("Expr_phe_cli_riskscore.RData")
riskScore_cli2 <- riskScore_cli %>%
inner_join(phe) %>%
column_to_rownames("sample") %>%
select(- "_PATIENT")
head(riskScore_cli2)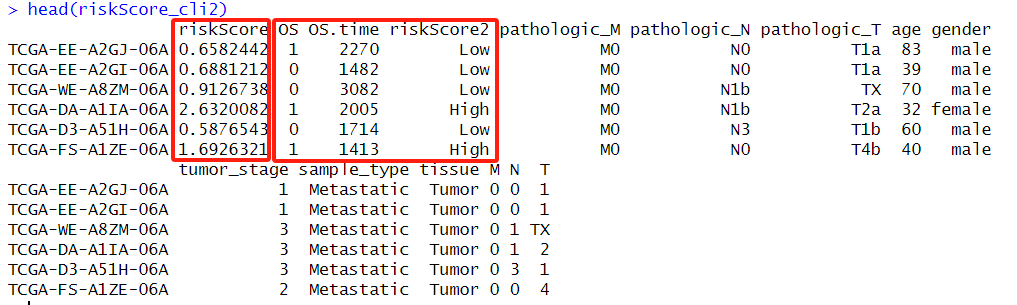

只要数据框中含有想展示的表型数据即可,一般会有风险得分,生存信息以及重要的临床指标,当然也可以其他重点关注的指标:(1)重点基因突变与否,例如KRAS突变 (2)某个CNV有无(3)TMB ,MSI,IDH等等你想展示的指标。如果添加基因表达量的话那就是正常的热图即可。
2,临床数据处理
在TCGA下载的临床数据需要进行一些处理,可以在excel中完成,当然也可以使用R完成。
包括但不限于以下(1)连续数值按照某个阈值转为分类 (2)向量和因子的转化 (3)将数据中的T1a ,T1b,T1 统一为T1期 类似的整理。
(1)和(2)比较简单,如下
#连续数值,按需转为分类
riskScore_cli2$Age =ifelse(riskScore_cli2$age > 60,">60","<=60")
#字符串转为因子
riskScore_cli2$OS <- as.factor(riskScore_cli2$OS)
riskScore_cli2$tumor_stage <- as.factor(riskScore_cli2$tumor_stage)(3)可以使用多种方式完成数据整理
A :T分期使用直接指定的方法
注意%in% c("T1a","T1b","T1")的向量中要列出所有想转化的,假设有T1c的话 也需要加上。
table(riskScore_cli2$pathologic_T)
# T0 T1 T1a T1b T2 T2a T2b T3 T3a T3b T4 T4a T4b Tis TX
# 23 10 21 10 30 32 15 14 39 37 13 26 109 7 44
riskScore_cli2$pathologic_T[riskScore_cli2$pathologic_T %in% c("T1a","T1b","T1")] <- "T1"
riskScore_cli2$pathologic_T[riskScore_cli2$pathologic_T %in% c("T2a","T2b","T2")] <- "T2"
riskScore_cli2$pathologic_T[riskScore_cli2$pathologic_T %in% c("T3a","T3b","T3")] <- "T3"
riskScore_cli2$pathologic_T[riskScore_cli2$pathologic_T %in% c("T4a","T4b","T4")] <- "T4"
table(riskScore_cli2$pathologic_T)B:N分期,使用gsub替换的方式
table(riskScore_cli2$pathologic_N)
# N0 N1 N1a N1b N2 N2a N2b N2c N3 NX
#226 17 19 37 6 13 21 9 56 34
riskScore_cli2$pathologic_N <- gsub("N1[abc]?", "N1", riskScore_cli2$pathologic_N)
riskScore_cli2$pathologic_N <- gsub("^N2.*", "N2", riskScore_cli2$pathologic_N)
riskScore_cli2$pathologic_N <- gsub("^N3.*", "N3", riskScore_cli2$pathologic_N)C:M分期,使用grepl的方法
table(riskScore_cli2$pathologic_M)
# M0 M1 M1a M1b M1c
#407 5 5 5 9
riskScore_cli2$pathologic_M <- ifelse(grepl("^M1", riskScore_cli2$pathologic_M),
"M1", riskScore_cli2$pathologic_M)
riskScore_cli2$pathologic_M <- ifelse(grepl("^M0", riskScore_cli2$pathologic_M),
"M0", riskScore_cli2$pathologic_M)D:还可以使用str_replace 或者 str_detect等方法进行转化,这里示例展示一下,不运行不影响推文的后续操作 。
riskScore_cli2$pathologic_T2 <- riskScore_cli2$pathologic_T
# str_replace
riskScore_cli2$pathologic_T2 <- str_replace(riskScore_cli2$pathologic_T2, "T1[a-d-c-d]?", "T1")
#str_detect
riskScore_cli2$pathologic_T2 <- ifelse(str_detect(riskScore_cli2$pathologic_T2, "^T1"), "T1", riskScore_cli2$pathologic_T2)以上就完成了本次分析需要的数据处理部分。
二 临床指标热图可视化
1,直接绘制
使用ComplexHeatmap绘制临床数据注释图 ,重点在于构建一个和临床数据相同列的0矩阵 。
# 提取想展示的临床数据
riskScore_cli2 <- riskScore_cli2 %>%
select(riskScore:tumor_stage,Age) %>%
select(- "age")
# 构建列注释块
ha=HeatmapAnnotation(df=riskScore_cli2)
# 构建zero矩阵
zero_row_mat=matrix(nrow=0, ncol=nrow(riskScore_cli2))
#绘制热图
Hm <- Heatmap(zero_row_mat, top_annotation=ha)
Hm
#调整legend的位置和大小
draw(Hm, merge_legend = TRUE,
heatmap_legend_side = "bottom",
annotation_legend_side = "bottom",
width = unit(16, "cm"), height = unit(1, "cm")
)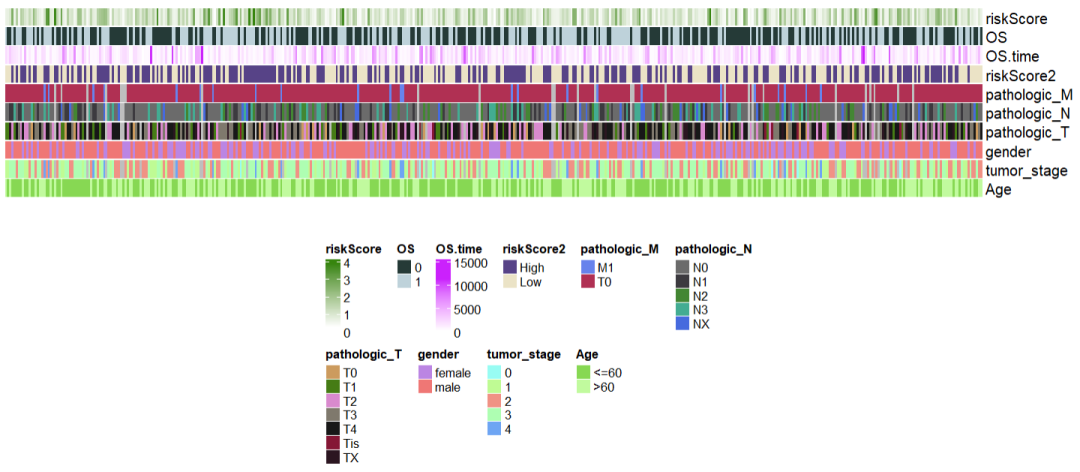
2,图形优化调整
上面可以顺利的完成图形可视化,相较文献还可以在(1)表型内容排序,比如优先Score高低排序,然后Stage排序(2)表型注释的顺序,比如先展示Score,然后OS,stage等 和(3)每种表型进行自定义的颜色设置 上进行优化和调整。
(1)表型内部排序 ,使用arrange 进行排序,可以依次选择多个指标
riskScore_cli3 <- riskScore_cli2 %>%
arrange(riskScore2,OS,tumor_stage,gender,OS.time,Age)(2)和(3)一起在HeatmapAnnotation注释中解决,如果为省事未展示T M N分期 ,可以自行添加。
library(circlize)
#连续性变量的颜色设置
col_fun_time <- colorRamp2(
c(0, 3000, 11000), #根据值的范围设置
c("#DC0000FF", "grey", "#1f78b4")
)
#
ha <- HeatmapAnnotation(
Score = riskScore_cli3$riskScore2,
Stage = riskScore_cli3$tumor_stage ,
OS.Status = riskScore_cli3$OS,
OS.Time = riskScore_cli3$OS.time,
Gender = riskScore_cli3$gender ,
Age = riskScore_cli3$Age,
col = list(
Score = c("High" = "#BC3C29FF", "Low" = "#0072B5FF"),
OS.Status = c("0" = "#E18727FF", "1" = "#20854EFF"), #分类
OS.Time = col_fun_time , #连续
Gender = c("female" = "#AB3282", "male" = "#3A6963"),
Age = c("<=60" = "#712820", ">60" = "#E4C755"),
Stage = c("0" = "#E64B35FF", "1" = "#4DBBD5FF",
"2" = "#00A087FF", "3" = "#3C5488FF",
"4" = "#DC0000FF", "NA" = "#8491B4FF")
)
)可视化展示
Hm <- Heatmap(zero_row_mat, top_annotation=ha)
draw(Hm, merge_legend = TRUE,
heatmap_legend_side = "bottom",
annotation_legend_side = "bottom",
width = unit(16, "cm"), height = unit(1, "cm")
)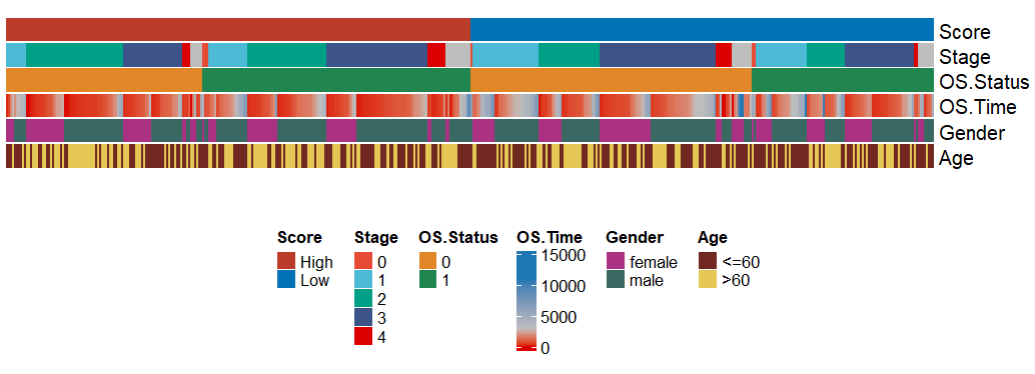
以上就完成了风险得分和临床指标的热图,拿去发文章吧。
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2024-04-18,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读
目录

