Seurat V5|一个函数就能解决多种去批次方法,按需尝试
Seurat V5|一个函数就能解决多种去批次方法,按需尝试

生信补给站
发布于 2023-12-19 13:14:08
发布于 2023-12-19 13:14:08
Seurat 是单细胞RNA数据分析的一个非常主流的R包,升级到当前V5版本后,会带来一些不友好的地方,但是也有一些功能上的升级,大家一定根据自己的情况和分析需求来确定是否升级。
V5的升级部分主要体现在以下4个方面(https://satijalab.org/seurat/articles/get_started_v5_new),本次先介绍第一个:Seurat V5中去批次方法的集成。
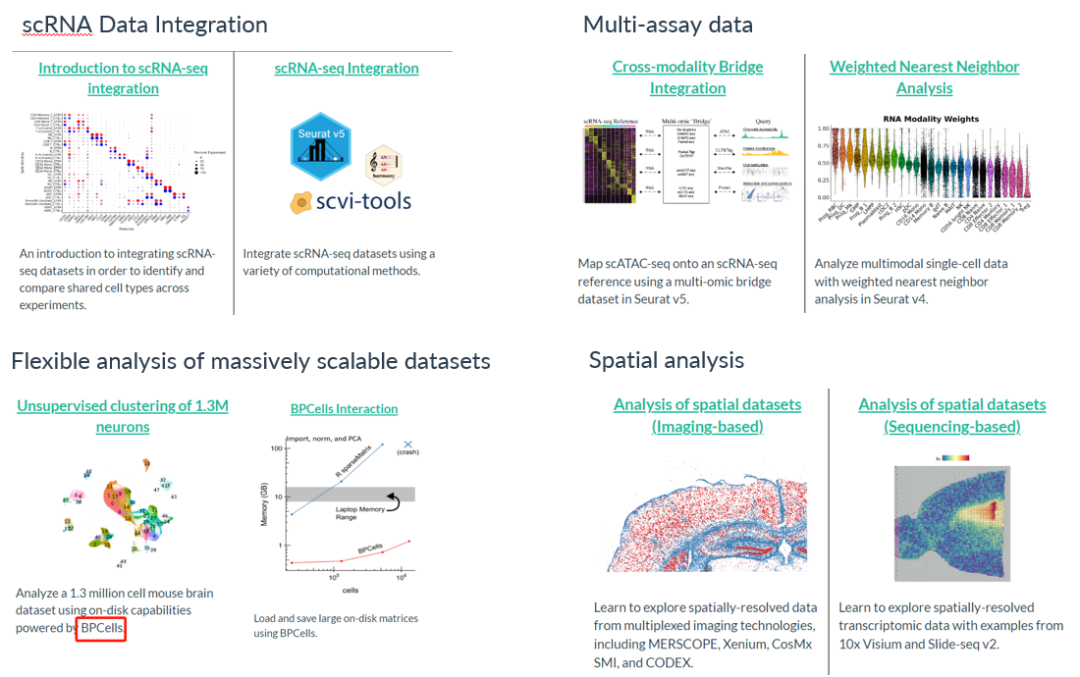
Seurat v5引入了更加灵活和精简的基础架构,可以用一行代码完成不同的集成去批次算法,极大的减少了不同方法的环境准备和数据处理时间,可以更聚焦在使用哪种方法效果更好。这使得探索不同集成方法的结果变得更加容易,并将这些结果与排除集成步骤的工作流进行比较。
本文以ifnb数据集作为示例,展示去批次的过程和方法。
一 R包,数据准备
1 载入R包
下载相关的R包,注意现在直接install.packages('Seurat')默认安装的就是V5版本。
library(Seurat)
library(SeuratData)
#remotes::install_github("satijalab/seurat-wrappers")
remotes::install_local("./seurat-wrappers-master.zip",upgrade = F,dependencies = F)
library(SeuratWrappers)
library(ggplot2)
library(patchwork)
options(future.globals.maxSize = 1e9)该系列会有较多的R包是在github中,可能存在无法安装的问题。
以satijalab/seurat-wrappers为例,当github的包无法下载时候,可以找到github地址然后点击Code,下载zip文件,
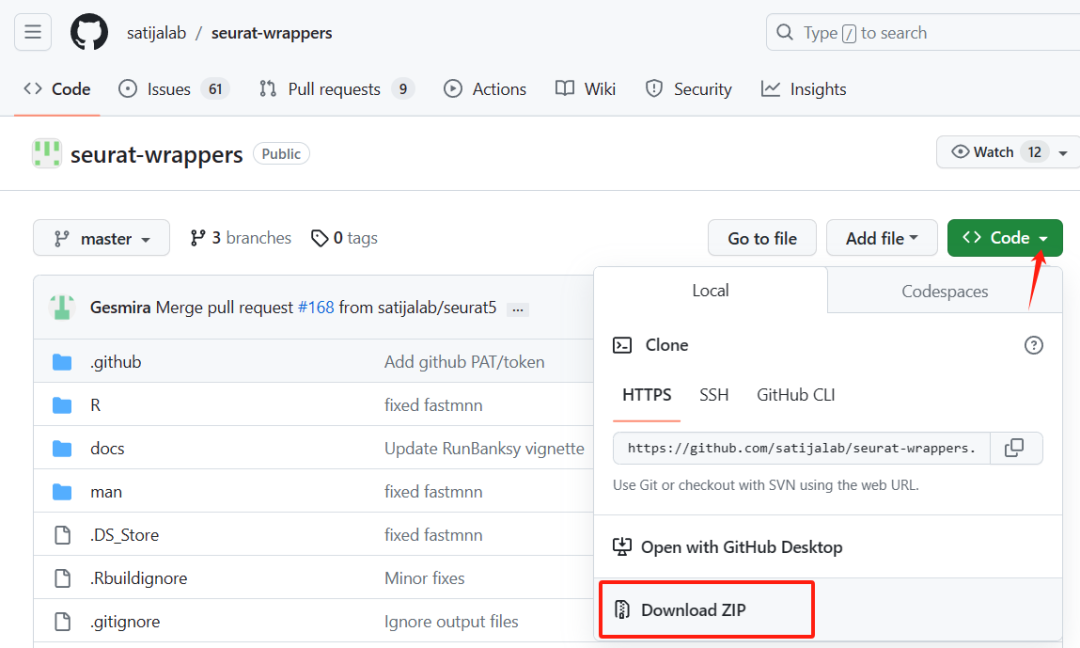
然后使用remotes::install_local的方式 本地安装。
2 下载示例数据
测试数据集同样在外网,受限于上网方式和网速,也大概率会报错。
无法下载的可以尝试下载到本地然后再安装(http://seurat.nygenome.org/src/contrib/ifnb.SeuratData_3.1.0.tar.gz),更多数据集的名称以及下载链接参考https://zhuanlan.zhihu.com/p/661800023https://zhuanlan.zhihu.com/p/661800023 。
# 下载测试数据集
#InstallData("ifnb")
install.packages('./ifnb.SeuratData_3.1.0.tar.gz', repos = NULL, type = "source")下载后载入数据,然后查看待处理的批次情况(stim列)
# load in the pbmc systematic comparative analysis dataset
obj <- LoadData("ifnb")
obj <- UpdateSeuratObject(obj)
obj <- subset(obj, nFeature_RNA > 1000)
obj
An object of class Seurat
14053 features across 1254 samples within 1 assay
Active assay: RNA (14053 features, 0 variable features)
2 layers present: counts, data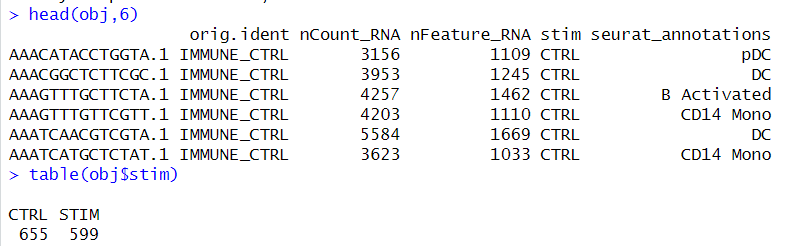
可以看到Seurat V5一个很大的变化就是layer。
二 数据整合(批次处理)
1,数据拆分
示例的Seurat对象中包含2种不同处理的数据(meta的stim列),使用Seurat v5 整合时是拆分为不同的layer 而无需拆分为多个对象。可以看到拆分后出现4个layer (stim列中的每个批次都有自己的count和data矩阵)。
Seurat V4 需要将数据拆分为2个不同的Seurat对象。
obj[["RNA"]] <- split(obj[["RNA"]], f = obj$stim)
obj
An object of class Seurat
14053 features across 1254 samples within 1 assay
Active assay: RNA (14053 features, 0 variable features)
4 layers present: counts.CTRL, counts.STIM, data.CTRL, data.STIM请注意,由于数据被分成几层,因此对每一批次独立执行归一化和HVG 。(自动识别一组一致的变量特征)。
obj <- NormalizeData(obj)
obj <- FindVariableFeatures(obj)
obj <- ScaleData(obj)
obj <- RunPCA(obj)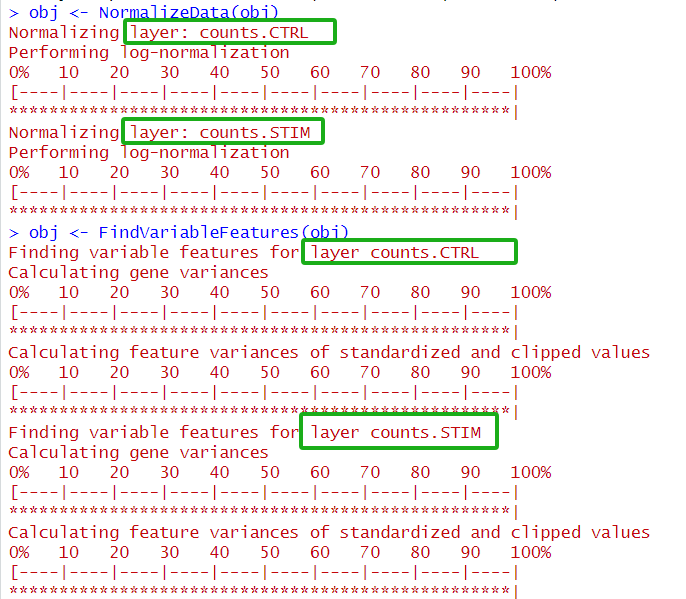
这里会针对每个“batch”分别进行NormalizeData 和 FindVariableFeatures。
2 数据直接合并(不去批次)
先尝试直接合并的方式,查看数据的批次情况
#直接整合
obj <- FindNeighbors(obj, dims = 1:30, reduction = "pca")
obj <- FindClusters(obj, resolution = 2, cluster.name = "unintegrated_clusters")
obj <- RunUMAP(obj, dims = 1:30,
reduction = "pca",
reduction.name = "umap.unintegrated")
DimPlot(obj, reduction = "umap.unintegrated",
group.by = c("stim", "seurat_annotations"))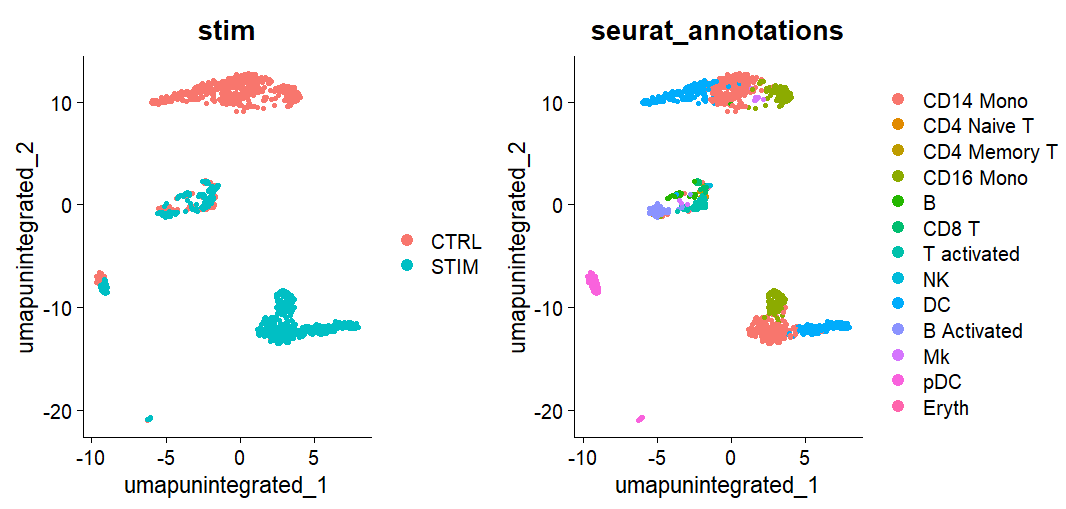
3,一行代码去批次
Seurat v5中的integratelayer函数支持一行代码完成去批次集成分析,当前支持以下五种主流的单细胞集成去批次方法。
- Anchor-based CCA integration (method=CCAIntegration)
- Anchor-based RPCA integration (method=RPCAIntegration)
- Harmony (method=HarmonyIntegration)
- FastMNN (method= FastMNNIntegration)
- scVI (method=scVIIntegration)
#CCA
obj <- IntegrateLayers(
object = obj, method = CCAIntegration,
orig.reduction = "pca", new.reduction = "integrated.cca",
verbose = FALSE
)
#RPCA
obj <- IntegrateLayers(
object = obj, method = RPCAIntegration,
orig.reduction = "pca", new.reduction = "integrated.rpca",
verbose = FALSE
)
#Harmony
obj <- IntegrateLayers(
object = obj, method = HarmonyIntegration,
orig.reduction = "pca", new.reduction = "harmony",
verbose = FALSE
)
#FastMNN
obj <- IntegrateLayers(
object = obj, method = FastMNNIntegration,
new.reduction = "integrated.mnn",
verbose = FALSE
)
obj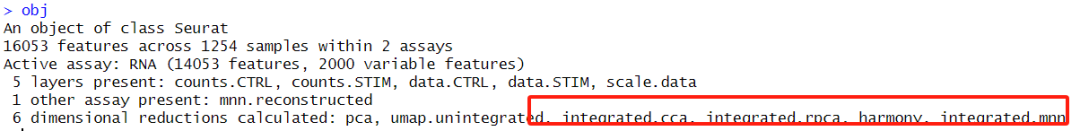
可见新增加了4种去批次方法,下面就是依次可视化,然后选择最终的方法继续后续分析。
还要注意定义new.reduction的名字,不然会被覆盖掉。
4,确定去批次方法
4.1 ,umap展示
这里用CCA 和 RPCA 示例,其他的两种同样的方式,注意修改reduction.name 。
#####CCA######
obj <- FindNeighbors(obj, reduction = "integrated.cca", dims = 1:30)
obj <- FindClusters(obj, resolution = 2, cluster.name = "cca_clusters")
obj <- RunUMAP(obj, reduction = "integrated.cca",
dims = 1:30,
reduction.name = "umap.cca")
p1 <- DimPlot(
obj,
reduction = "umap.cca",
group.by = c("Method", "CellType", "cca_clusters"),
combine = FALSE, label.size = 2
)
#####RPCA######
obj <- FindNeighbors(obj, reduction = "integrated.rpca", dims = 1:30)
obj <- FindClusters(obj, resolution = 2, cluster.name = "rpca_clusters")
obj <- RunUMAP(obj, reduction = "integrated.rpca",
dims = 1:30,
reduction.name = "umap.rpca")
p2 <- DimPlot(
obj,
reduction = "umap.rpca",
group.by = c("Method", "CellType", "rpca_clusters"),
combine = FALSE, label.size = 2
)
wrap_plots(c(p1, p2), ncol = 2, byrow = F)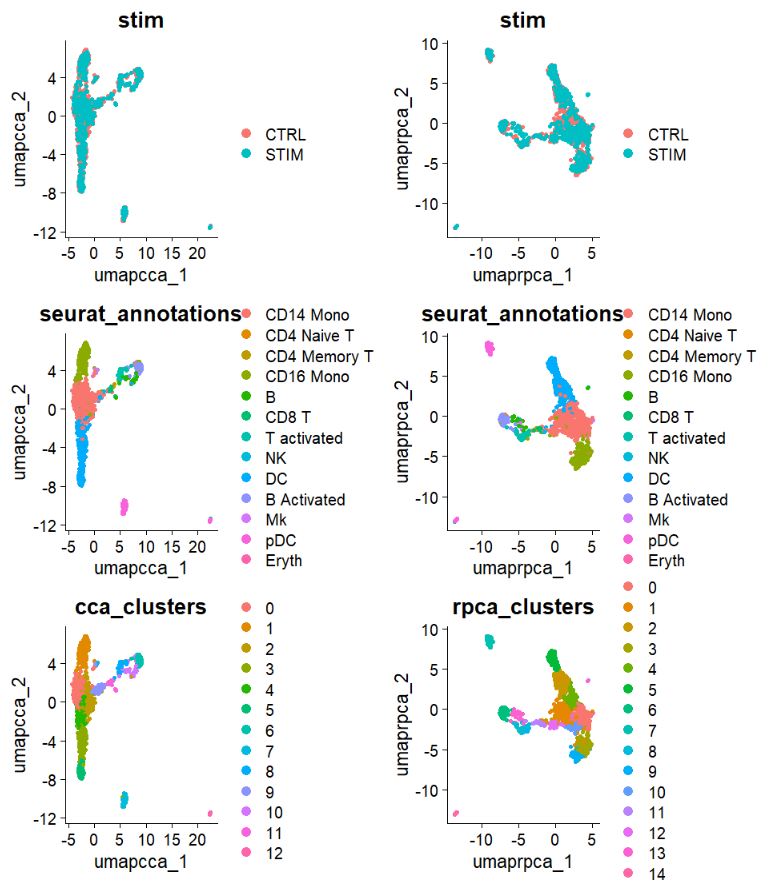
对比直接合并,可以看到不同stim之间的批次效应被整合,可以加上另两种同时展示4种方法,现在一种进行后续的分析。
4.2 Marker 可视化
还可以利用经典marker比较不同去批次方法的表现
(1)VlnPlot 图
p1 <- VlnPlot(
obj,
features = "rna_CD8A", group.by = "unintegrated_clusters") +
NoLegend() + ggtitle("CD8A - Unintegrated Clusters")
p2 <- VlnPlot(
obj, "rna_CD8A",
group.by = "cca_clusters") +
NoLegend() + ggtitle("CD8A - CCA Clusters")
p3 <- VlnPlot(
obj, "rna_CD8A",
group.by = "rpca_clusters") +
NoLegend() + ggtitle("CD8A - RPCA Clusters")
p1 | p2 | p3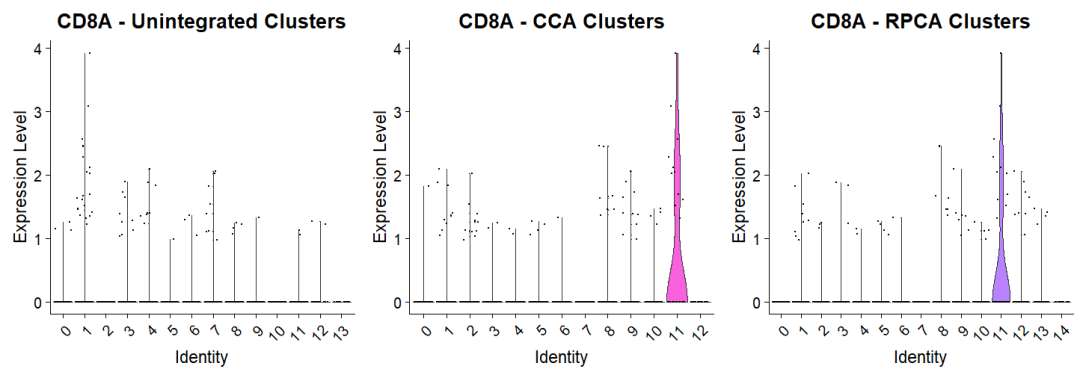
(2)DimPlot 图
p4 <- DimPlot(obj, reduction = "umap.unintegrated", group.by = c("cca_clusters"))
p5 <- DimPlot(obj, reduction = "umap.rpca", group.by = c("cca_clusters"))
p6 <- DimPlot(obj, reduction = "umap.cca", group.by = c("cca_clusters"))
p4 | p5 | p6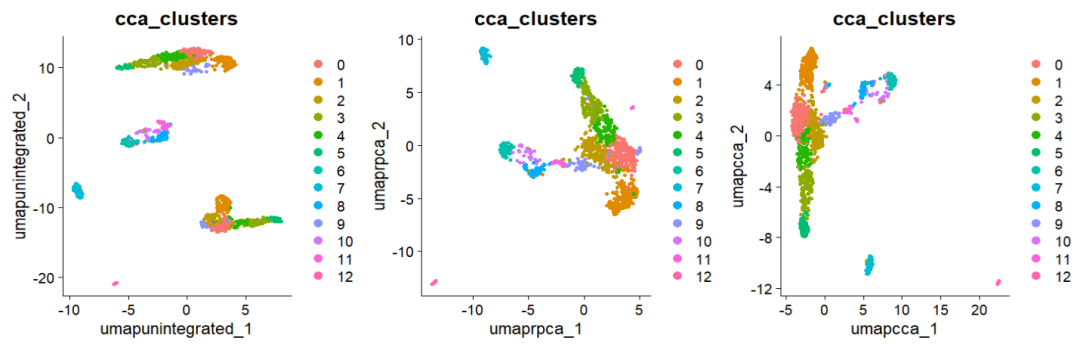
根据以上的信息确定最终使用的去批次方法。
三 FindMarker 分析
确定去批次方法后,就可以进行FindMarker 以及注释。
1,rejoin layer
要注意当前的layer是根据stim批次拆分开的,在进行任何的differential expression analysis之前都要先使用JoinLayers函数进行rejoin the layers 。
obj
obj2 <- JoinLayers(obj) #仅为了区分,实际情况下使用obj即可
obj2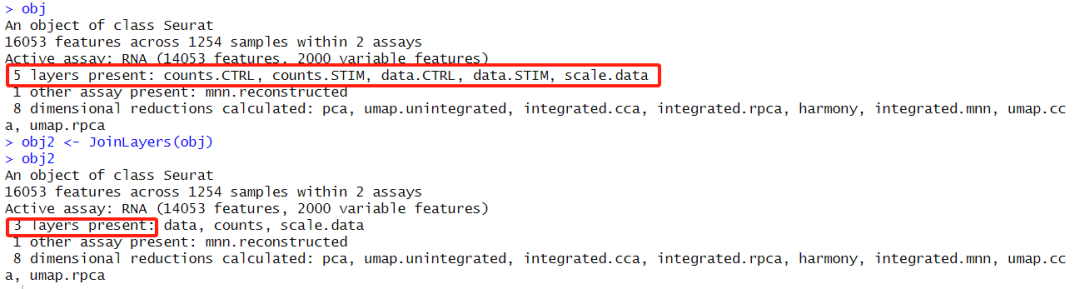
接下来就是DEG分析,找到各个cluster的marekr基因进行手动注释或者直接使用singleR等自动注释软件完成注释。
参考资料:
https://satijalab.org/seurat/articles/seurat5_integration
https://satijalab.org/seurat/articles/integration_introduction
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2023-12-18,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读
目录

