人生第一次使用Kobas注释基因功能
原创KOBAS 是北京大学整合多个数据库,进行基因功能注释的平台,包含在线版和Docker版。KOBAS
多组基因注释时,用Docker版注释更加方便,开启Docker初尝试。
Step1 Download Docker
需要下载 Koabs.tar文件,我使用的是第一个。

Kobas 文件
Step2 开启Docker镜像
接下来的部分在Linux在完成,本人使用的Ubuntu系统
newgrp docker # 无Root 权限运行Docker(服务器平常用户没有Root权限)
docker load -i kobas.tar # 导入Kobas镜像
docker images # 检测 Kobas 镜像是否导入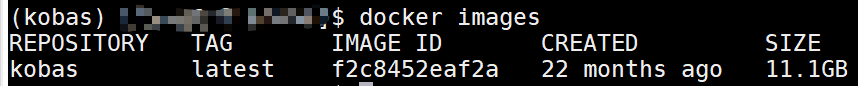
Docker 镜像 已经导入
Step3 开始使用Kobas
docker run -it -v local/workspace/旋转木马/software/kobas:/opt/gene_enrich kobas:latest
# local/workspace/旋转木马/ 为原Linux中的路径
# :/opt/gene_enrich 为新容器中的路径Step4 开始使用Kobas
进行功能富集前需要进行基因注释
使用前annotate.py -h / identify.py -h 查看帮助文档
# 基因注释
annotate.py -i c1.txt -t id:gene_symbol -s mmu -o anno_c1.txt # c1.txt 差异基因,anno-差异基因注释后的结果
# 功能富集
identify.py -f anno_c1.txt -o iden_c1.txt # 得到结果 iden_c1.txt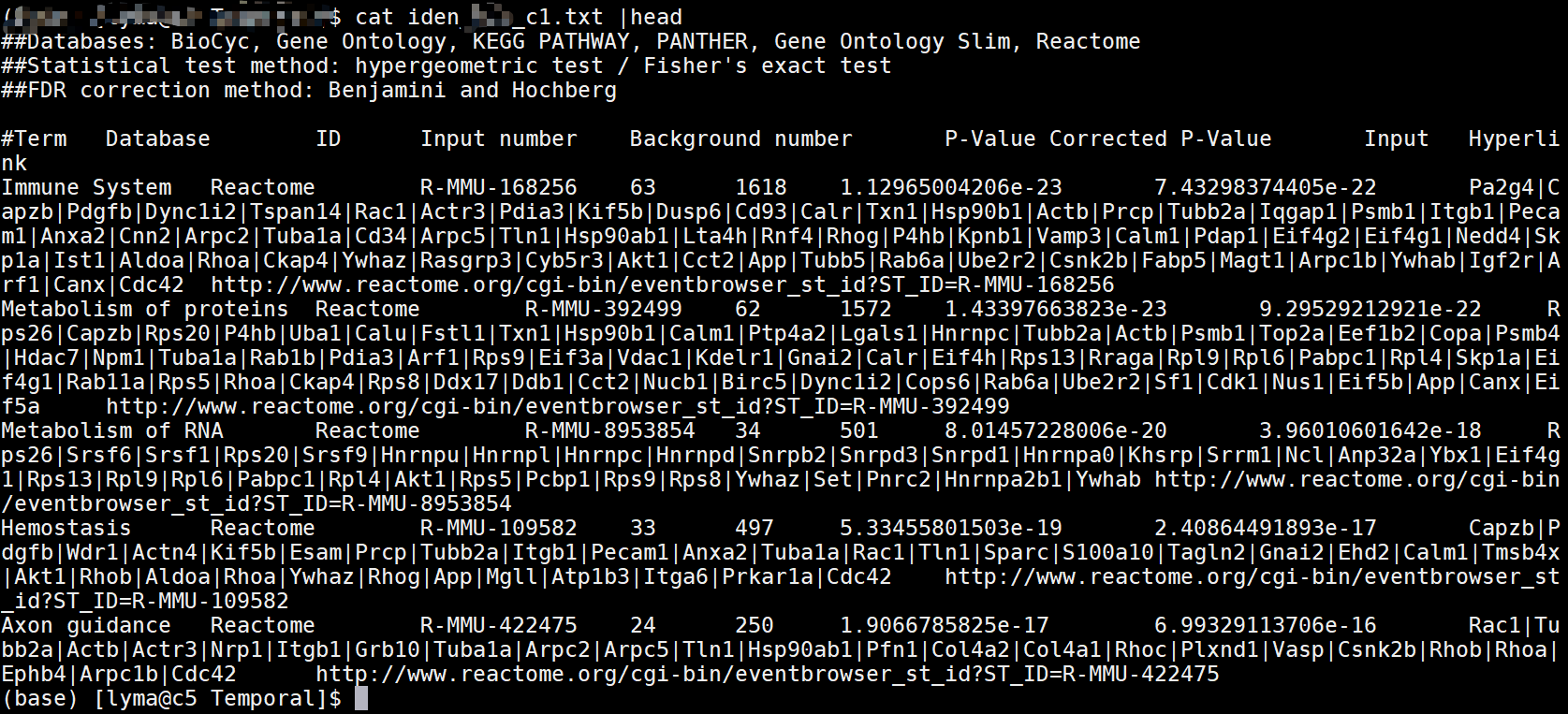
得到以上结果
后续使用该信息,进行可视化
原创声明:本文系作者授权腾讯云开发者社区发表,未经许可,不得转载。
如有侵权,请联系 cloudcommunity@tencent.com 删除。
原创声明:本文系作者授权腾讯云开发者社区发表,未经许可,不得转载。
如有侵权,请联系 cloudcommunity@tencent.com 删除。
评论
登录后参与评论
推荐阅读
目录


