细菌综述 IF8.5 Q1 | NGS在细菌感染研究和控制中的应用
细菌综述 IF8.5 Q1 | NGS在细菌感染研究和控制中的应用

简说基因
发布于 2025-11-12 14:04:00
发布于 2025-11-12 14:04:00

本文发表于 2018 年,虽然年代有点久远了,但是对于微生物研究来说还是具有参考价值。在 google 学术中显示有 630 个引用,在 PubMed 中显示有 199 次引用。
本文先是简要介绍了测序技术的发展过程:
- • DNA 测序技术自 1970 年代初就已存在,但最初其成本和复杂性,以及对有毒或放射性试剂的要求限制了它们在研究环境中的使用。
- • Sanger 方法(“第一代”技术)是 1975 年至 2005 年间的主要测序技术。Sanger 测序产生相对较长(500e1000 bp)的高质量 DNA 序列,长期以来一直被认为是 DNA 测序的参考标准。
- • 2005 年,454 Life Sciences(美国康涅狄格州布兰福德)引入焦磷酸测序技术,开启了 NGS 革命。
- • 由于第二代测序平台的短读长往往会产生相对碎片化的基因组组装,因此需要更长的读长才能生成封闭的参考基因组。在对复杂的基因组区域(如重复序列和噬菌体)进行测序时,长读长特别有用。一些噬菌体的长度可达 50-75 kb。为了满足这一需求,引入了所谓的第三代测序平台。
分析方法
分子流行病学的基本假设之一是:系统发育近似于流行病学传播路径。具体而言,若致使患者患病的病原体在系统发育上密切相关,则这些患者之间存在流行病学关联的可能性,远高于病原体无亲缘关系的情况。
同理,若源自食物或环境的病原体与临床分离株在系统发育上相关,则两者很可能存在因果关系。通过序列分析产生可重复且具有系统发育意义的数据,是将序列数据实际应用于疫情检测与调查的核心所在。
在分型领域,目前主要采用两种高分辨力的系统发育方法:
- • 高质量单核苷酸多态性分析(hqSNP)
- • 核心基因组/全基因组多位点序列分型(cg/wgMLST)
hqSNP 方法通过将菌株与单一参考基因组比对,分析其间的单核苷酸差异。该参考基因组必须与比对菌株亲缘相近,方能识别出真正具有系统发育信息量的 SNP 位点。使用不同参考基因组和分析流程得出的结果无法直接比较。由于参考基因组的选择难以标准化——几乎所有疫情都需要独特的参考菌株,且众多 hqSNP 分析工具(流程)中缺乏选用共识——该方法不太适用于多实验室同步开展的疫情调查。然而,在集中化分析场景下,hqSNP 表现出色,其菌株分辨能力与 wgMLST 相当或更优。
cg/wgMLST 方法则更具普适性。全基因组多位点序列分型(wgMLST)评估某一特定属或物种中理论上全部基因的多样性;核心基因组多位点序列分型(cgMLST)则分析该属或物种中普遍存在的所有基因。新发现的菌株会与包含所有已知基因变异的等位基因数据库进行比对,该数据库可用于评估其所属物种所有菌株间的亲缘关系。随着此类数据库数量的持续增长(部分已公开共享),MLST 方法展现出对多实验室联合疫情调查的独特适应性——例如 PulseNet 网络开展的协同研究便是典型范例。
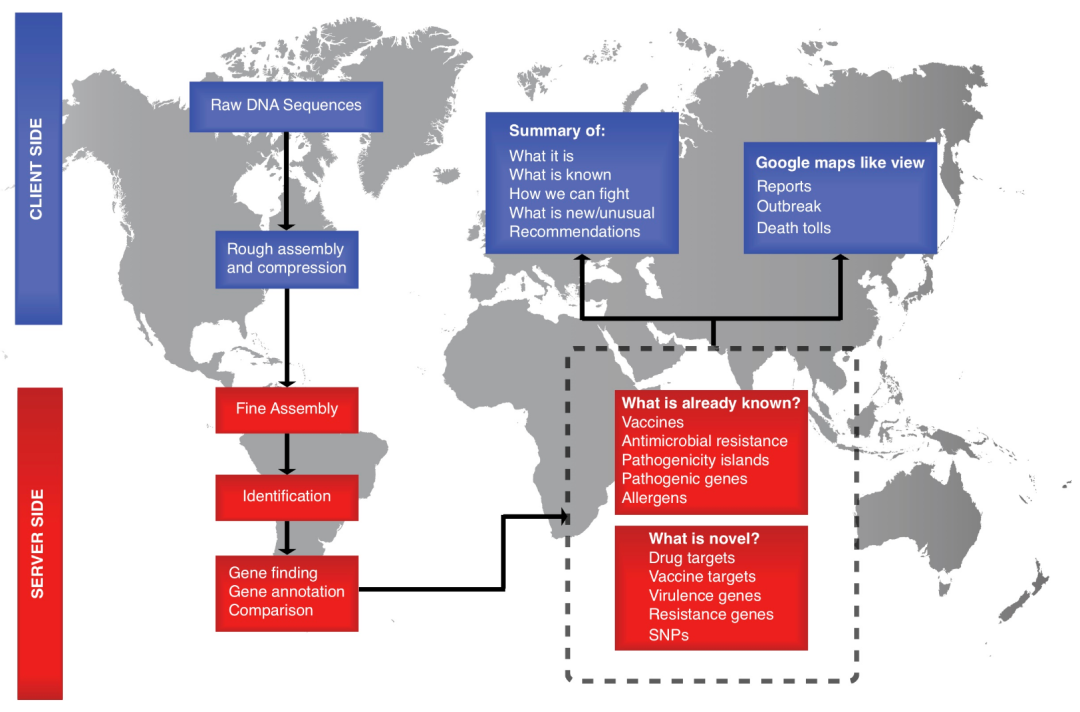
如今,微生物学家即使不具备深厚的生物信息学背景,也能通过网络获取分析工具完成病原体特征分析,这大大加速了鉴定流程。例如,细菌全基因组测序(WGS)的计算机分析工具可在基因组流行病学中心(CGE)网站(www.genomicepidemiology.org)获取。该平台除其他功能外,还提供毒力基因预测(VirulenceFinder)、耐药性分析(ResFinder)及血清型鉴定(SerotypeFinder)等工具,适用于大肠杆菌等致病菌的分析。CGE 网站还设有集成化分析流程,可对批量序列同时执行多项分析任务。
自 20 世纪 60 年代起,DNA-DNA 杂交(DDH)便被视为物种鉴定的金标准。1987 年,韦恩(Wayne)提出将 70%及以上的 DDH 相似度作为判定菌株属于同一物种的标准。全基因组测序(WGS)时代对应的 DDH 替代方法是平均核苷酸一致性(ANI)。该方法通过计算两个菌株共有基因组区域的核苷酸匹配度,能够直接从 WGS 数据中明确鉴定菌株物种归属。约 95%的 ANI 值相当于 60%-70%的 DDH 值。对芽孢杆菌属、伯克霍尔德菌属、埃希氏菌/志贺氏菌属、假单胞菌属、希瓦氏菌属和链球菌属的 28 个基因组序列进行分析显示,同种菌株间的 ANI 值均达到 95%以上。
ANI 算法(ANIm)可在数秒至数分钟内完成菌株物种鉴定。该算法基于 MUMMER 软件运行,该软件集成了快速全基因组比对工具,并能使用多参考基因组构建数据库,从而实现查询序列的快速比对。
未来展望
测序、数据传输和分析的成本将继续降低,DNA 纯化包括文库制备和实际测序将变得更快、更高效。当前长读长技术的致命弱点,即高错误率,将继续改进,直到它们变得像短读长技术一样精确,届时后者将过时。
自动化对于该技术在临床微生物学中的常规使用至关重要。目前,大型临床和公共卫生实验室的测序程序越来越自动化。标准化数据处理和分析也正在开发为在线(www.genomicepidemiology.org;www.ncbi.nlm.nih.gov/pathogens/)或独立应用程序。NGS 发展的下一步将是将测序和数据分析这两者整合到一个高效的工作流程中。
从长远来看,改进的长读长技术与更高效的 IT 能力、核酸富集技术和生物信息学相结合,将使标本宏基因组学测序的常规实施成为可能,用于非培养临床诊断、真正的实时感染控制和公共卫生监测。
小编总结
本文简单介绍了测序技术的发展,然后提及了几种细菌分型的办法:
- • 高质量单核苷酸多态性分析(high-quality single nucleotide polymorphisms,hqSNP)
- • 核心基因组/全基因组多位点序列分型(core genome/whole genome multilocus sequence typing,cg/wgMLST)
- • 平均核苷酸一致性(Average Nucleotide Identity,ANI)
展望未来,作者认为随着长读长技术的不断完善,必将取代当前的短读长技术。另外自动化生物信息学分析管道也非常重要,比如:
- • www.genomicepidemiology.org
- • www.ncbi.nlm.nih.gov/pathogens
作者还认为,未来随着生物和 IT 技术的不断发展,微生物的宏基因组学测序将成为常规手段。
推荐阅读
中国银河生信云平台(UseGalaxy.cn)致力于零代码生信分析。平台拥有海量计算资源、3000 多个生信工具和数十条生信流程,并且为用户提供 200G 免费存储空间。我们还为进阶用户提供高质量课程培训:
本文参与 腾讯云自媒体同步曝光计划,分享自微信公众号。
原始发表:2025-11-10,如有侵权请联系 cloudcommunity@tencent.com 删除
评论
登录后参与评论
推荐阅读
目录

